RNK

Ribonukleinska kiselina (RNK) je biološki važan tip molekula koji se sastoji od dugih kovalentno vezanih jedinica nukleotida. Svaki nukleotid se sastoji od nukleobaze, šećera riboze i fosfata. RNK je veoma slična DNK, ali se od nje razlikuje u nekoliko važnih strukturnih detalja. RNK u ćelijama se sastoji iz jedne zavojnice dok je kod DNK dvostruka zavojnica, dok RNK nukleotide čine riboza i uracil za razliku od DNK koja se sastoji od deoksiriboze (tip riboze kojoj nedostaje jedan atom kiseonika) i timina.
RNK nastaje transkripcijom DNK pomoću enzima koji se nazivaju RNK polimeraze, a dalje se procesira preko drugih enzima. Uloga RNK u sintezi bjelančevina je nezamjenjiva. U tom procesu, vrsta RNK koja se naziva prijenosna RNK prenosi informacije sadržane u vidu aminokiselina sa DNK na strukture koje se nazivaju ribozomi. Ovi ribozomi su načinjeni iz bjelančevina i ribozomske RNK, koji zajedno formiraju molekularnu mašinu za čitanje prijenosne RNK i prevodi informacije koje ona prenosi u bjelančevine. Postoji mnogo vrsta RNK sa različitim ulogama: od određenih reguliranja kako je pojedini gen izražen do sačinjavanja genoma većine virusa.
Struktura[uredi | uredi kod]
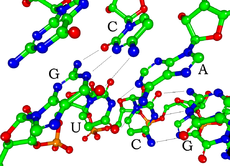
Svaki nukleotid u RNK sadrži šećer ribozu, sa atomima ugljika označenim od 1 do 5. Baza je spojena na poziciju 1, obično je na poziciju 3 jedne molekule riboze spojena fosfatna grupa i na poziciju 5 slijedeće riboze. Fosfatne grupe imaju negativni naboj, svaka sa fiziološkom pH vrijednošću, čineći RNK molekulu polianionom. Baze mogu formirati vodonikove veze između citozina i guanina, između adenina i uracila te između guanina i uracila[1]. Međutim, moguće su i druge interakcije, poput međusobnog povezivanja grupe adeninskih baza[2] ili kao tetrakružni GNRA koji ima guanin-adenin bazni par[1].

Važna strukturalna osobina RNK koja je razlikuje od DNK je prisustvo hidroksil grupe na poziciji 2 šećera riboze. Prisustvo ove funkcionalne grupe uzrokuje da zavojnica poprimi geometriju A-forme DNK umjesto B-forme koja je obično prisutna u DNK[3]. Ova osobina dovodi do veoma dubokih i uskih glavnih brazda i plitkih i širokih sporednih brazda u molekuli[4]. Druga posljedica prisustva hidroksilne grupe na drugoj poziciji je ta da konformaciono fleksibilna područja molekule RNK (ona koja nisu uključena u formiranje dvostruke zavojnice) mogu hemijski napasti susjedne fosfodiesterske veze vezane na kostur zavojnice[5].
RNK se transkribira sa samo četiri baze (adenin, citozin, guanin i uracil) [6], ali postoje brojne izmijenjene baze i šećeri u starijim molekulama RNK. Pseudouridin, u kojem je veza između uracila i riboze izmjenjena iz C-N veze u C-C vezu, te ribotimidin (T) su pronađeni na raunim mjestima (među najznačajnijim u T?C zavoju u transportnoj RNK)[7]. Druga značajna izmijenjena veza je hipoksantin, deaminizirana adeninska baza čiji se nukleosid naziva inosin (I). Inosin igra ključnu ulogu u dinamičkoj hipotezi genetskog koda[8]. Postoji gotovo 100 drugih prirodnih izmijenjenih nukleosida[9], od kojih su najčešći pseudouridin i nukleosid sa 2'-0-metilribozom[10]. Detaljne uloge mnogih od ovih modifikacija u RNK nisu u potpunosti istražene. Međutim, značajno je da se u ribozomskoj RNK pojavljuju mnoge od post-transkripcijskih modifikacija u visoko funkcionalnim područjima, poput središta peptidil transferaze i interfejsu podjedinica, što vodi do zaključka da su veoma važne za normalne funkcije[11].
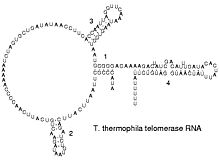
Funkcionalna forma jednostruko uvijene molekule RNK, poput bjelančevina, često zahtijeva određene tercijarne RNK strukture. Osnova za ovu strukturu je zasnovana na sekundarnim strukturalnim elementima koji su u principu vodonikove veze unutar molekule. Ovo dovodi do nekoliko prepoznatljivih domena sekundarne strukture poput zašiljenih prstenova, unutrašnjih prstenova i deformacija[12]. Pošto je RNK molekula sa naelektrisanjem, ioni metala poput magnezijuma Mg2+ su neophodni za stabilizaciju mnogih sekundarnih i tercijarnih struktura[13].
Usporedba sa DNK[uredi | uredi kod]
RNK i DNK su nukleinske kiseline, ali se razlikuju u tri važna elementa. Prvo, za razliku od DNK koja je dvostruka zavojnica, molekula RNK je samo jednostruko uvijena u većini svojih bioloških uloga i ima daleko manji lanac nukleotida. Drugo, dok DNK sadržo šećer deoksiribozu, RNK sadrži ribozu (u kojoj nema hidroksil funkcionalne grupe spojene na pentozni prsten na poziciji 2' kod DNK). Ove hidroksilne grupe čine RNK manje stabilnom molekulom od DNK jer su daleko podložnije hidrolizi. Treće, komplementarna baza adeninu nije timin, kao što je slučaj kod DNK, nego je uracil, koji je nemetilirana forma timina[14].
Poput DNK, biološki najaktivnije RNK poput mRNK, tRNK, rRNK i druge nekodne RNK, sadrže sekvence komplementarne sebi koje omogućavaju dijelovima RNK da se dijele i uparuju sa samom sobom obrazujući na taj način dvostruke zavojnice. Strukturalna analiza ovih RNK je otkrila da su one veoma kompleksno struktuirane. Za razliku od DNK, ove strukture se ne sadrže iz dugih dvostrukih zavojnica, već od nakupina kratkih zavojnica spojenih zajedno u strukture dosta slične bjelančevinama.
Na ovaj način, molekule RNK mogu biti podvrgnute hemijskoj katalizi, poput enzima[15]. Na primjer, proučavanje strukture ribozima - enzima koji katalizira formiranje peptidne veze - otkriva da je njegovo aktivno mjesto sastavljeno u potpunosti iz RNK[16].
Sinteza[uredi | uredi kod]
Sinteza RNK se obično katalizira djelovanje enzima - RNK polimeraze - koristeći DNK kao šablon, što je proces poznat kao transkripcija. Pokretanje trankripcije uređuje vezivanje enzima na sekvencu promotera u DNK (obično se nalazi iznad gena u zavojnici). Dvostruka zavojnica DNK se odmotava djelovanjem enzima helikaze. Enzim zatim napreduje u pravcu šablona u smijeru od 3' prema 5' vezi, sintetizirajući komplementarnu RNK molekulu sa izduženjem u smijeru od 5' prema 3' vezi. DNK sekvenca također određuje kada će se desiti prekid sinteze RNK[17]. Molekule RNK se često mogu izmijeniti nakon transkripcije djelovanjem enzima.
Postoji i veliki broj RNK polimeraza koje zavise od RNK i koje koriste RNK kao svoj šablon za sintezu novih lanaca RNK. Na primjer, veliki broj RNK virusa (kao što je poliovirus) koriste ovaj tip enzima za repliciranje svog genetskog materijala[18]. Također, RNK zavisna RNK polimeraza je dio interferentne putanje RNK u mnogim organizmima[19].
Vrste RNK[uredi | uredi kod]
Pregled[uredi | uredi kod]

Informacijska RNK (iRNK) je RNK koja prenosi informacije od DNK do ribozoma, mjesta u ćeliji gdje se vrši sinteza bjelančevina (translacija). Kodna sekvenca iRNK određuje sekvencu aminokiselina u bjelančevinama koje se trebaju proizvoditi[20]. Međutim, mnoge RNK se ne kodiraju za proizvodnju bjelančevina (oko 97% transkripcijskog izlaza su informacije koje se ne odnose na kodiranje bjelančevina kod eukariotskih ćelija[21][22][23][24]).
Ove takozvane ne-kodne RNK (nkRNK) se mogu dekodirati putem vlastitih gena (RNK gena), ali se mogu i derivirati iz introna iRNK[25]. Najpoznatiji primjeri nekodnih RNK su transportne RNK (tRNK) i ribozomske RNK (rRNK). Obje ove vrste RNK su uključene u proces translacije[14]. Postoje i nekodne RNK koje su uključene u regulaciju gena, procesiranje RNK i druge uloge. Određene RNK imaju mogućnost da kataliziraju hemijske reakcije poput isjecanja i vezivanja drugih RNK molekula[26], te katalizu formiranja peptidnih veza u ribozomima;[16] te RNK su poznate i kao ribozimi.
Translacija[uredi | uredi kod]
Informacijska RNK (iRNK) prenosi informacije o sekvencama bjelančevina u ribozomima, organelama u ćeliji gdje se sintetiziraju bjelančevine. One su tako kodirane da su neopdhona tri nukleotida (kodon) da se sintetiše jedna aminokiselina. U eukariotskim ćelijama, nakon što se inicijalna iRNK prepiše sa originalnog mjesta u DNK, prenosi se do zrele iRNK. Ona uklanja initrone inicijalne iRNK, njene nekodne dijelove. Zatim se iRNK izvozi iz ćelijskog jedra u citoplazmu, gdje se veže na ribozome i translatira u odgovarajuću formu bjelančevinu uz pomoć tRNK. U prokariotskim ćelijama, koje nemaju organele koje odgovaraju jedru i citoplazmi, iRNK se može vezati za ribozome istovremeno dok se prepisuje sa DNK. Nakon određenog vremena, informacije se degradiraju u svoje nukleotidne komponente uz pomoć ribonukleaze[20].
Transportna RNK (tRNK) je malehni RNK lanac od oko 80 nukleotida koji prenosi određene aminokiseline prilikom translacije u rastući polipeptidni lanac na ribozomskom mjestu sinteze bjelančevina. Ona ima mjesta za pripajanje aminokiselina i antikodonski region za prepoznavanje kodona na koji se spaja određena sekvenca na lanacu iRNK putem vodikovih veza[25].
Ribozomska RNK (rRNK) je katalitička komponenta ribozoma. Eukariotski ribozomi sadrže četiri različite rRNK molekule: 18S, 5.8S, 28S i 5S rRNK. Tri od ove rRNK molekule se sintetiziraju u jedarcetu, dok se jedna sintetizira drugdje. U citoplazmi, rRNK i bjelančevine se kombiniraju u formi nukleobjelančevina zvanih ribozomi. Ribozomi vežu iRNK, a u njima se odvija sinteza bjelančevina. Nekoliko ribozoma može biti istovremeno vezano na jednu iRNK[20]. rRNK je veoma raširena u ćeliji, čini oko 80% uzorka od 10 mg/ml RNK ekstraktovane iz tipične eukariotske citoplazme[27].
Transportno-informaciona RNK (tiRNK) je pronađena u mnogim bakterijama i plastidima. Ona označava bjelančevine dekodirane od iRNK kojima nedostaju zaustavni kodoni za degradaciju te onemogućavaju prekid rada ribozoma[28].
Regulatorne RNK[uredi | uredi kod]
Postoji nekoliko tipova RNK koje mogu deregulirati izražavanje gena tako što djeluju kao komplementarni dio iRNK ili DNK gena.
Mikro RNK (miRNK (miRNA); 21-22 nt) su pronađene u eukariotskim ćelijama i djeluju putem RNK interference (RNKi), gdje kompleks efektora miRNK i enzimi mogu razdvojiti iRNK koja je komplementarna miRNK, blokirati iRNK tako da ona ne može biti prevedena ili ubrzati proces njene degradacije[29][30].
Postoje također i male interferne RNK (miRNK (siRNA); 20-25 nt) koje često nastaju razgradnjom RNK virusa, a postoje i endogeni izvori miRNK (siRNA)[31][32]. miRNK (siRNA) mogu djelovati i preko RNK interference slično kao i kod miRNK (miRNA). Neke miRNK (miRNA) i miRNK (siRNA) mogu na određenim ciljnim genima prouzrokovati metiliranje, te tako usporiti ili ubrzati transkripciju tih gena[33][34][35]. Životinjske ćelije imaju piwi-interakcionu RNK (piRNK (piRNA); 29-30 nt) koja je aktivna u spolnim ćelijama i smatraju se da predstavljaju odbranu protiv transposona te igraju ulogu pri gametogenezi[36][37]. Mnoge prokariotske ćelije imaju CRISPR RNK, regulatorni sistem sličan RNK interferenci[38].
Antisense RNK su široko rasprostranjene, najviše kao deregulatori gena, a nekoliko od njih su aktivatori transkripcije[39]. Jedan od načina kako antisense RNK može djelovati je putem vezivanja na iRNK formirajući tako dvospiralnu zavojnicu RNK koja se enzimski degradira[40]. Postoji veliki broj dugih nekodnih RNK koje regulišu gene u eukariotskim ćelijama[41], jedna od tih RNK je Xist koja prekriva jedan X kromosom u ženkama sisara i deaktivira ga[42].
iRNK i sama može sadržavati regulatorne elemente, poput riboprekidača, u 5' neprevedenom regionu ili 3' neprevedenom regionu; ovi cis-regulatorni elementi reguliraju aktivnosti te iRNK[43]. Neprevedeni regioni također mogu sadržavati elemente koji reguliraju druge gene[44].
Otkriće[uredi | uredi kod]
Nukleinske kiseline su otkrivene 1868. godine. Otkrio ih je Friedrich Miescher, koji je otkrivene supstance nazivao nuklein jer su nađene u ćelijskom jedru[45]. Kasnije je otkriveno da prokariotske ćelije, koje nemaju ćelijsko jedro, također sadržavaju nukleinske kiseline. Uloga RNK u sintezi bjelančevina je pretpostavljena već od 1939. godine[46]. Naučnik Severo Ochoa je dobio Nobelovu nagradu za medicinu 1959. godine nakon što je otkrio način sinteze RNK[47]. Sekvenca od 77 nukleotida kod tRNK plijesni je otkrivena 1965. godine od strane Robert W Holleya[48], što je Holleyju donijelo Nobelovu nagradu za medicinu 1968. godine.
Godine 1967, Carl Woese je iznio teoriju da RNK može djelovati kao katalizator te je pretpostavio da su se najraniji oblici života zasnivali na RNK koja im je služila i kao genetski materijal a ujedno je i vršila kataliziranje biohemijskih reakcija. Ta teorija je poznata i kao hipoteza RNK svijeta[49][50].
Godine 1976, tim naučnika na čelu sa Walter Fiersom je otkrio prvu potpunu nukleotidnu sekvencu RNK genoma virusa, i to od bakteriofaga MS2[51].
Godine 1990, pronađeno je da strani geni koji su uneseni u biljku petuniju mogu da onemoguće slične gene koji su prisutni u biljci, što je danas poznato i kao interferencija RNK[52][53]. Otprilike u istom periodu, otkrivene su ribonukleinske kiseline duge 22 nukleotida, danas poznate kao mikroRNK, a koje imaju ulogu u razvoju nematode Caenorhabditis elegans[54].
Otkriće regulatornih RNK u genu je dovela do pokušaja da se razviju lijekovi na bazi RNK, kao što je siRNK, u svrhu onemogućavanja djelovanja određenih gena[55].
Povezano[uredi | uredi kod]
- Genetika
- Molekularna biologija
- Sinteza oligonukleotida
- Ekstrakcija ribonukleinske kiseline
- Struktura ribonukleinske kiseline
Vanjske veze[uredi | uredi kod]
- RNA World web stranica Arhivirano 2007-03-14 na Wayback Machine-u Kolekcija linkova o RNK (strukture, sekvence, alati, žurnali)
- Baza podataka o nukleinskim kiselinama Arhivirano 2007-10-12 na Wayback Machine-u Slike DNK, RNK i kompleksa.
Reference[uredi | uredi kod]
- ↑ 1,0 1,1 Lee JC, Gutell RR (2004). „Diversity of base-pair conformations and their occurrence in rRNA structure and RNA structural motifs”. J. Mol. Biol. 344 (5): 1225-49.
- ↑ Barciszewski J, Frederic B, Clark C (1999). RNA biochemistry and biotechnology. Springer. str. 73-87. ISBN 0-7923-5862-7
- ↑ Salazar M, Fedoroff OY, Miller JM, et al. (1992). „The DNA strand in DNAoRNA hybrid duplexes is neither B-form nor A-form in solution”. Biochemistry 32 (16): 4207-15.
- ↑ Hermann T, Patel DJ (2000). „RNA bulges as architectural and recognition motifs”. Structure 8 (3): R47-R54.
- ↑ Mikkola S, Nurmi K, Yousefi-Salakdeh E, et al. (1999). „The mechanism of the metal ion promoted cleavage of RNA phosphodiester bonds involves a general acid catalysis by the metal aquo ion on the departure of the leaving group”. Perkin transactions 2: 1619-26.
- ↑ Jankowski JAZ, Polak JM (1996). Clinical gene analysis and manipulation: Tools, techniques and troubleshooting. Cambridge University Press. str. 14. ISBN 0-521-47896-0
- ↑ Yu Q, Morrow CD (2001). „Identification of critical elements in the tRNA acceptor stem and T?C loop necessary for human immunodeficiency virus type 1 infectivity”. J Virol 75 (10): 4902-6.
- ↑ Elliott MS, Trewyn RW (1983). „Inosine biosynthesis in transfer RNA by an enzymatic insertion of hypoxanthine”. J. Biol. Chem. 259 (4): 2407-10.
- ↑ Söll D, RajBhandary U (1995). TRNA: Structure, biosynthesis, and function. ASM Press. str. 165. ISBN 1-55581-073-X
- ↑ Kiss T (2001). „Small nucleolar RNA-guided post-transcriptional modification of cellular RNAs”. The EMBO Journal 20: 3617-22.
- ↑ King TH, Liu B, McCully RR, Fournier MJ (2002). „Ribosome structure and activity are altered in cells lacking snoRNPs that form pseudouridines in the peptidyl transferase center”. Molecular Cell 11 (2): 425-35.
- ↑ Mathews DH, Disney MD, Childs JL, et al. (2004). „Incorporating chemical modification constraints into a dynamic programming algorithm for prediction of RNA secondary structure”. Proc. Natl. Acad. Sci. USA 101 (19): 7287-92.
- ↑ Tan ZJ, Chen SJ (2008). „Salt dependence of nucleic acid hairpin stability”. Biophys. J. 95 (2): 738-52.
- ↑ 14,0 14,1 Berg JM, Tymoczko JL, Stryer L (2002). Biochemistry (5. izd. izd.). WH Freeman and Company. str. 118-19, 781-808. ISBN 0-7167-4684-0
- ↑ Higgs PG (2000). „RNA secondary structure: physical and computational aspects”. Quarterly Reviews of Biophysics 33: 199-253.
- ↑ 16,0 16,1 Nissen P, Hansen J, Ban N et al. (2000). „The structural basis of ribosome activity in peptide bond synthesis”. Science 289 (5481): 920-30.
- ↑ Nudler E, Gottesman ME (2002). „Transcription termination and anti-termination in E. coli”. Genes to Cells 7: 755-68.
- ↑ Jeffrey L Hansen, Alexander M Long, Steve C Schultz (1997). „Structure of the RNA-dependent RNA polymerase of poliovirus”. Structure 5 (8): 1109-22.
- ↑ Ahlquist P (2002). „RNA-Dependent RNA Polymerases, Viruses, and RNA Silencing”. Science 296 (5571): 1270-73.
- ↑ 20,0 20,1 20,2 Cooper GC, Hausman RE (2004). The Cell: A Molecular Approach (3. izd. izd.). Sinauer. str. 261-76, 297, 339-44. ISBN 0-87893-214-3
- ↑ Mattick JS, Gagen MJ (2001-09-01). „The evolution of controlled multitasked gene networks: the role of introns and other noncoding RNAs in the development of complex organisms”. Mol. Biol. Evol. 18 (9): 1611-30.
- ↑ Mattick, J.S. (2001). "Noncoding RNAs: the architects of eukaryotic complexity" Arhivirano 2005-12-27 na Wayback Machine-u, EMBO Reports, 2(11), 986-991.
- ↑ Mattick, J.S. (2003). "Challenging the dogma: The hidden layer of non-protein-coding RNAs on complex organisms" Arhivirano 2009-03-06 na Wayback Machine-u, Bioessays. 25, 930-939.
- ↑ Mattick, J.S. (2004): "The hidden genetic program of complex organisms", Scientific American. 291(4), 30-37.
- ↑ 25,0 25,1 Wirta W (2006). Mining the transcriptome - methods and applications. Stockholm: School of Biotechnology, Royal Institute of Technology. ISBN 91-7178-436-5
- ↑ Rossi JJ (2004). „Ribozyme diagnostics comes of age”. Chemistry & Biology 11 (7): 894-95.
- ↑ Kampers T, Friedhoff P, Biernat J, et al. (1996). „RNA stimulates aggregation of microtubule-associated protein tau into Alzheimer-like paired helical filaments”. FEBS Letters 399 (3): 104D.[mrtav link]
- ↑ Gueneau de Novoa P, Williams KP (2004). „The tmRNA website: reductive evolution of tmRNA in plastids and other endosymbionts”. Nucleic Acids Res. 32 (Database issue): D104-8.
- ↑ Wu L, Belasco JG (January 2008). „Let me count the ways: mechanisms of gene regulation by miRNAs and siRNAs”. Mol. Cell 29 (1): 1-7.
- ↑ Matzke MA, Matzke AJM (2004). „Planting the seeds of a new paradigm”. PLoS Biology 2 (5): e133.
- ↑ Vazquez F, Vaucheret H, Rajagopalan R, et al. (2004). „Endogenous trans-acting siRNAs regulate the accumulation of Arabidopsis mRNAs”. Molecular Cell 16 (1): 69-79.
- ↑ Watanabe T, Totoki Y, Toyoda A, et al. (May 2008). „Endogenous siRNAs from naturally formed dsRNAs regulate transcripts in mouse oocytes”. Nature 453 (7194): 539-43.
- ↑ Sontheimer EJ, Carthew RW (July 2005). „Silence from within: endogenous siRNAs and miRNAs”. Cell 122 (1): 9-12.
- ↑ Doran G (2007). „RNAi - Is one suffix sufficient?”. Journal of RNAi and Gene Silencing 3 (1): 217-19. Arhivirano iz originala na datum 2007-07-16. Pristupljeno 2010-08-23.
- ↑ Pushparaj PN, Aarthi JJ, et al. (2008). „RNAi and RNAa - The Yin and Yang of RNAome”. Bioinformation 2 (6): 235-7.
- ↑ Horwich MD, Li C Matranga C, et al. (2007). „The Drosophila RNA methyltransferase, DmHen1, modifies germline piRNAs and single-stranded siRNAs in RISC”. Current Biology 17: 1265-72.
- ↑ Girard A, Sachidanandam R, Hannon GJ, Carmell MA (2006). „A germline-specific class of small RNAs binds mammalian Piwi proteins”. Nature 442: 199-202.
- ↑ Horvath P, Barrangou R (2010). „CRISPR/Cas, the Immune System of Bacteria and Archaea”. Science 327: 167.
- ↑ Wagner EG, Altuvia S, Romby P (2002). „Antisense RNAs in bacteria and their genetic elements”. Adv Genet. 46: 361-98.
- ↑ Gilbert SF (2003). Developmental Biology (7. izd. izd.). Sinauer. str. 101-3. ISBN 0-87893-258-5
- ↑ Amaral PP, Mattick JS (October 2008). „Noncoding RNA in development”. Mammalian genome 19 (7-8): 454.
- ↑ Heard E, Mongelard F, Arnaud D, et al. (1999). „Human XIST yeast artificial chromosome transgenes show partial X inactivation center function in mouse embryonic stem cells”. Proc. Natl. Acad. Sci. USA 96 (12): 6841-46.
- ↑ Batey RT (2006). „Structures of regulatory elements in mRNAs”. Curr. Opin. Struct. Biol. 16 (3): 299-306.
- ↑ Scotto L, Assoian RK (June 1993). „A GC-rich domain with bifunctional effects on mRNA and protein levels: implications for control of transforming growth factor beta 1 expression”. Mol. Cell. Biol. 13 (6): 3588-97.
- ↑ Dahm R (2005). „Friedrich Miescher and the discovery of DNA”. Developmental Biology 278 (2): 274-88.
- ↑ Caspersson T, Schultz J (1939). „Pentose nucleotides in the cytoplasm of growing tissues”. Nature 143: 602-3.
- ↑ Ochoa S (1959). „Enzymatic synthesis of ribonucleic acid”. Nobel Lecture.
- ↑ Holley RW et al. (1965). „Structure of a ribonucleic acid”. Science 147 (1664): 1462-65.
- ↑ Siebert S (2006). „Common sequence structure properties and stable regions in RNA secondary structures”. Dissertation, Albert-Ludwigs-Universität, Freiburg im Breisgau. str. 1. Arhivirano iz originala na datum 2012-03-09. Pristupljeno 2010-08-23.
- ↑ Szathmáry E (1999). „The origin of the genetic code: amino acids as cofactors in an RNA world”. Trends Genet. 15 (6): 223-9.
- ↑ Fiers W et al. (1976). „Complete nucleotide-sequence of bacteriophage MS2-RNA: primary and secondary structure of replicase gene”. Nature 260 (5551): 500-7.
- ↑ Napoli C, Lemieux C, Jorgensen R (1990). „Introduction of a chimeric chalcone synthase gene into petunia results in reversible co-suppression of homologous genes in trans”. Plant Cell 2 (4): 279-89.
- ↑ Dafny-Yelin M, Chung SM, et al. (December 2007). „pSAT RNA interference vectors: a modular series for multiple gene down-regulation in plants”. Plant Physiol. 145 (4): 1272-81.
- ↑ Ruvkun G (2001). „Glimpses of a tiny RNA world”. Science 294 (5543): 797-99.
- ↑ Fichou Y, Férec C (2006). „The potential of oligonucleotides for therapeutic applications”. Trends in Biotechnology 24 (12): 563-70.
